Se ha mencionado anteriormente que el impacto de las ciencias ómicas en la medicina contemporánea, se debe en gran parte al análisis de grandes volúmenes de datos (Big data).
En el caso de las ER, los grandes volúmenes de datos originados de la biología molecular, son difíciles de correlacionar con la clínica dado el escaso número de pacientes, de tal forma que la conformación de registros de pacientes y familias afectadas por ER, se constituye en una herramienta fundamental para recabar la mayor cantidad de sujetos que contribuyan a la comprensión de la enfermedad (98).
Los registros digitales y la captura electrónica de datos son un aspecto rutinario de la investigación, de hecho, la historia clínica electrónica es un tipo de registro, sin embargo, para los registros de las ER se deben contemplar las características clínicas especiales de estas enfermedades, las cuales deben tenerse en cuenta en el momento de diseñar los formulario de captura y en el momento de listar las variables a considerar (99).
Además, dado el contexto social de las ER (vulnerabilidad, discriminación y barreras de acceso a la salud) los registros deben hacer particular énfasis en la privacidad, seguridad y confidencialidad de los datos (100, 101).
Por tanto, la educación médica debe considerar el entrenamiento en el registro de datos, en la correcta codificación de las enfermedades (Ej.: entrenamiento en el uso adecuado del CIE-10) y en el reconocimiento de la importancia que los registros tienen en la comprensión de la enfermedad, tanto a nivel clínico como a nivel de salud pública. (Lea también: Efectos de las Citocinas)
Esta valoración acerca de la importancia de los registros en las ER se extiende nuevamente al resto de la Medicina, debido a que el registro adecuado de los diagnósticos clínicos, independientemente de si son o no ER o si se trata enfermedades de notificación obligatoria, es el que permite la construcción de perfiles epidemiológicos y el análisis de datos de prevalencia locales, a partir de los cuales es posible establecer, desde políticas de salud pública, hasta protocolos de investigación.
Los registros clínicos van de la mano con la construcción de Biobancos (repositorios de muestras biológicas), los cuales son un componente fundamental de la medicina personalizada, dado que respaldan el descubrimiento y validación de biomarcadores, así como la estratificación de las poblaciones en razón a variables de interés clínicos y biológicos (102).
Los Biobancos, en el caso de las ER son valiosos instrumentos de investigación, dado que comprenden un conjunto de información demográfica y clínica relacionada con cada muestra biológica, la cual puede ser almacenada para investigaciones futuras o para el desarrollo de investigación in vitro e in sillico.
El registro de pacientes y el Biobanco hacen parte de la cotidianidad de ciertas especialidades médicas como patología y genética, sin embargo, la introducción de la bioinformática, junto con la necesidad de análisis de datos masivos (Big Data) y la introducción de nuevas técnicas de análisis molecular (Ej.: Secuenciación de Nueva Generación) ha obligado a las instituciones que manejan muestras, a formalizar y estructurar los repositorios.
De tal forma que tengan objetivos de acuerdo a una orientación poblacional (Biobancos enfocados en el estudio del desarrollo de enfermedades prevalentes) o hacia enfermedad específica (Biobancos enfocados en el estudio del desarrollo de enfermedades específicas, como pueden ser las ER) (102).
En el desarrollo de registros clínicos y Biobancos, se conjugan aspectos éticos y legales, ciencias ómicas, bioinformática, epidemiología y salud pública, alrededor de una estructura de gestión de la información biomédica que soporta la investigación traslacional.
Las facultades de Medicina no pueden ser ajenas a estos desarrollos y deben incluir dentro del entrenamiento de sus estudiantes al menos las nociones básicas que les permitan a los médicos del futuro, comprender las relaciones que existen entre la práctica médica, los Registros y los Biobancos.
Conclusiones
El pensum tradicional de la Medicina, basado en la correlación anatomo-fisiológica y anatomo-patológica, está siendo enriquecido por la comprensión de los mecanismos moleculares de la enfermedad, conocimientos que están llegando al punto de hacer posible y efectiva clínicamente, la edición de genes, la terapia génica y la clonación terapéutica (103, 104).
Diversas áreas de investigación biomédica avanzaban y se desarrollan para conformar nuevas disciplinas que harán parte de la rutina de la atención médica, muchos de estos desarrollos surgieron del estudio de las ER y posteriormente, utilizando la misma metodología, fueron instalándose en las investigaciones de las enfermedades multifactoriales y prevalentes.
Es así como además de cobrar cada vez mayor importancia en el ámbito asistencial, las ER ha sido un pilar importante en la construcción de una nueva medicina, de tal forma que las facultades, deben preparar a sus médicos tanto en el conocimiento y atención optima de las ER y el fortalecimiento de las ciencias básicas.
Como en la aplicación de métodos bioinformáticos y gestión de la información biomédica, apegadas a principios éticos sólidamente consolidados en la práctica y con total conocimiento y aplicación de la normatividad y leyes vigentes. Algunas de esas repercusiones se representan en la figura 1.
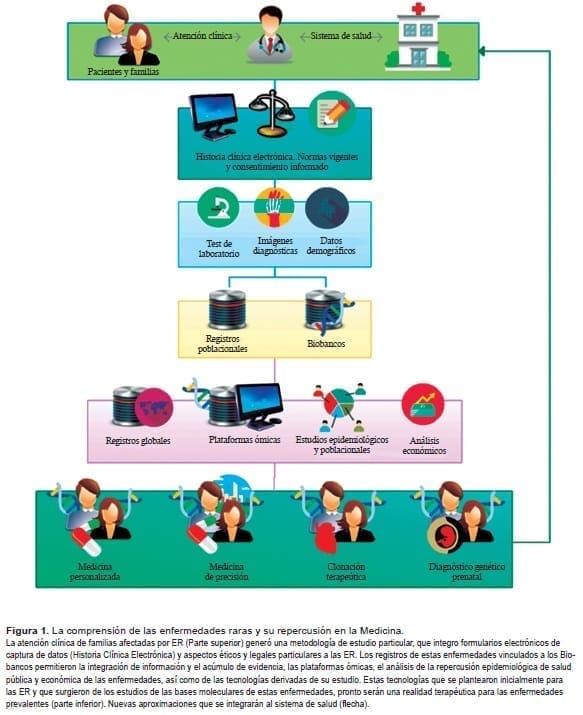
Las ER generan retos en la atención médica que repercuten en todas las áreas de enseñanza de la medicina y mientras la biotecnología avanza al ritmo vertiginoso del progreso científico, la educación médica debe integrar nuevas áreas de conocimiento que preparen adecuadamente a los médicos del futuro.
La educación médica no puede rezagarse del actual desarrollo, de otra forma, el modelo actual será prontamente caduco y no colmará las expectativas de salud de la población, ni responderá adecuadamente a los desafíos asistenciales de la enfermedad.
Conflicto de intereses
El autor no tiene ningún conflicto de interés que declarar.
Referencias
1. Song P, Gao J, Inagaki Y, Kokudo N, Tang W. Rare diseases, orphan drugs, and their regulation in Asia: Current status and future perspectives. Intractable Rare Dis Res. 2012;1(1):3-9.
2. Aronson JK. Rare diseases and orphan drugs. Br J Clin Pharmacol. 2006;61(3):243-5.
3. Rare Diseases Act of 2002. Public Law 107-280 2002 [Available from: https://www.gpo.gov/fdsys/pkg/PLAW-107publ280/html/PLAW-107publ280.htm.
4. Haffner ME, Whitley J, Moses M. Two decades of orphan product development. Nat Rev Drug Discov. 2002;1(10):821-5.
5. Forman J, Taruscio D, Llera VA, Barrera LA, Cote TR, Edfjall C, et al. The need for worldwide policy and action plans for rare diseases. Acta Paediatr. 2012;101(8):805-7.
6. Franco P. Orphan drugs: the regulatory environment. Drug Discov Today. 2013;18(3-4):163-72.
7. Dallari S. Fornecimento do medicamento pós-estudo em caso de doenças raras: conflito ético. Revista Bioética. 2015;23(2).
8. Congreso de Colombia. Ley 1438 de 2011. Por medio de la cual se reforma el Sistema General de Seguridad Social en Salud y se dictan otras disposiciones. 2011.
9. Bavisetty S, Grody WW, Yazdani S. Emergence of pediatric rare diseases: Review of present policies and op-portunities for improvement. Rare Dis. 2013;1:e23579.
10. Barrera LA, Galindo GC. Ethical aspects on rare diseases. Adv Exp Med Biol. 2010;686:493-511.
11. Gulbakan B, Ozgul RK, Yuzbasioglu A, Kohl M, Deigner HP, Ozguc M. Discovery of biomarkers in rare diseases: innovative approaches by predictive and personalized medicine. EPMA J. 2016;7:24.
12. Litterman NK, Rhee M, Swinney DC, Ekins S. Collaboration for rare disease drug discovery research. F1000Res. 2014;3:261.
13. Camp KM, Krotoski D, Parisi MA, Gwinn KA, Cohen BH, Cox CS, et al. Nutritional interventions in primary mito-chondrial disorders: Developing an evidence base. Mol Genet Metab. 2016;119(3):187-206.
14. Finkel RS, Mercuri E, Darras BT, Connolly AM, Kuntz NL, Kirschner J, et al. Nusinersen versus Sham Control in Infantile-Onset Spinal Muscular Atrophy. N Engl J Med. 2017;377(18):1723-32.
15. Beck M. Treatment strategies for lysosomal storage disorders. Dev Med Child Neurol. 2018;60(1):13-8.
16. Fishman MC, Porter JA. Pharmaceuticals: a new grammar for drug discovery. Nature. 2005;437(7058):491-3.
17. Morales-Piga A, Garcia Ribes M, Arribas Alvaro P, Casado Alvaro C, Posada de La Paz M, Bachiller-Corral J. [Is there a place in primary care for rare diseases? The case of fibrodysplasia ossificans progressiva]. Aten Primaria. 2013;45(6):324-8.
18. Senior T, Knight A. Rare diseases: a role for primary care. Lancet. 2008;372(9642):890.
19. Pariser AR, Gahl WA. Important role of translational science in rare disease innovation, discovery, and drug development. J Gen Intern Med. 2014;29 Suppl 3:S804-7.
20. Thevenon J, Duffourd Y, Masurel-Paulet A, Lefebvre M, Feillet F, El ChERadER-Djebbar S, et al. Diagnostic odyssey in severe neurodevelopmental disorders: toward clinical whole-exome sequencing as a first-line diagnostic test. Clin Genet. 2016;89(6):700-7.
21. Basel D, McCarrier J. Ending a Diagnostic Odyssey: Family Education, Counseling, and Response to Eventual Diagnosis. Pediatr Clin North Am. 2017;64(1):265-72.
22. Lazaridis KN, Schahl KA, Cousin MA, Babovic-Vuksanovic D, Riegert-Johnson DL, Gavrilova RH, et al. Outcome of Whole Exome Sequencing for Diagnostic Odyssey Cases of an Individualized Medicine Clinic: The Mayo Clinic Experience. Mayo Clin Proc. 2016;91(3):297-307.
23. Potter BK, Chakraborty P, Kronick JB, Wilson K, Coyle D, Feigenbaum A, et al. Achieving the “triple aim” for inborn errors of metabolism: a review of challenges to outcomes research and presentation of a new practice-based evidence framework. Genet Med. 2013;15(6):415-22.
24. Hawkes CP, Walsh A, O’Sullivan S, Crushell E. Doctors’ knowledge of the acute management of Inborn Errors of Metabolism. Acta Paediatr. 2011;100(3):461-3.
25. Camp KM, Lloyd-Puryear MA, Yao L, Groft SC, Parisi MA, Mulberg A, et al. Expanding research to provide an evidence base for nutritional interventions for the management of inborn errors of metabolism. Mol Genet Metab. 2013;109(4):319-28.
26. Zand DJ, Brown KM, Lichter-Konecki U, Campbell JK, SalERi V, Chamberlain JM. Effectiveness of a clinical pathway for the emergency treatment of patients with inborn errors of metabolism. Pediatrics. 2008;122(6):1191- 5.
27. Camp KM, Lloyd-Puryear MA, Huntington KL. Nutritional treatment for inborn errors of metabolism: indications, regulations, and availability of medical foods and dietary supplements using phenylketonuria as an example. Mol Genet Metab. 2012;107(1-2):3-9.
28. Leonard JV, Morris AA. Diagnosis and early management of inborn errors of metabolism presenting around the time of birth. Acta Paediatr. 2006;95(1):6-14.
29. Valayannopoulos V, Poll-The BT. Diagnostic work-up in acute conditions of inborn errors of metabolism and storage diseases. Handb Clin Neurol. 2013;113:1553-62.
30. Grosse SD, Wordsworth S, Payne K. Economic methods for valuing the outcomes of genetic testing: beyond cost-effectiveness analysis. Genet Med. 2008;10(9):648-54.
31. Lopez-Bastida J, Oliva-Moreno J. Cost of illness and economic evaluation in rare diseases. Adv Exp Med Biol. 2010;686:273-82.
32. Winter SC, Buist NR. Inborn errors of metabolism: medical and administrative “orphans”. Am J Manag Care. 1998;4(8):1164-8.
33. Novoa MC, Burnham TF. [Challenges for the universalization of clinical genetics: the Brazilian case]. Rev Pa-nam Salud Publica. 2011;29(1):61-8.
34. Paez P, Suarez-Obando F, Zarante I. [Genetic diseases in pediatric patients hospitalised in the town of Ubate, Colombia]. Rev Salud Publica (Bogota). 2008;10(3):414- 22.
35. Rolfo C, Caglevic C, Bretel D, Hong D, Raez LE, Cardona AF, et al. Cancer clinical research in Latin America: current situation and opportunities. Expert opinion from the first ESMO workshop on clinical trials, Lima, 2015. ESMO Open. 2016;1(4):e000055.
36. de la Fuente J, Martuscelli J, Alarcón–Segovia D. El futuro de la investigación médica en México. Gac Méd Méx 2004;40(5):519-24.
37. Kalergis AM, Lacerda M, Rabinovich GA, Rosenstein Y. Challenges for Scientists in Latin America. Trends Mol Med. 2016;22(9):743-5.
38. Zúñiga J. La enseñanza de las ciecnias básicas en medicina desde la perspectiva de la justificación epistemo-lógica del curriculo. Educación. 2009;33(2).
39. Bellgard MI, Sleeman MW, Guerrero FD, Fletcher S, Baynam G, Goldblatt J, et al. Rare Disease Research Roadmap: Navigating the bioinformatics and translational challenges for improved patient health outcomes. Health Policy and Technology. 2014;3(4):325-35.
40. Benitez-Paez A, Cardenas-Brito S. [Bioinformatics in Colombia: state of the art and perspectives]. Biomedica. 2010;30(2):170-7.
41. Weber SL, Segal S, Packman W. Inborn errors of metabolism: psychosocial challenges and proposed family systems model of intervention. Mol Genet Metab. 2012;105(4):537-41.
42. Baldovino S, Moliner AM, Taruscio D, Daina E, Roccatello D. Rare Diseases in Europe: from a Wide to a Local Perspective. Isr Med Assoc J. 2016;18(6):359-63.
43. Feltmate K, Janiszewski PM, Gingerich S, Cloutier M. Delayed access to treatments for rare diseases: who’s to blame? Respirology. 2015;20(3):361-9.
44. Jamiolkowski D, Kolker S, Glahn EM, Baric I, Zeman J, Baumgartner MR, et al. BERavioural and emotional pro-blems, intellectual impairment and health-related quality of life in patients with organic acidurias and urea cycle disorders. J Inherit Metab Dis. 2016;39(2):231-41.
45. República de Colombia. Ministerio de la Protección Social. Ley 1392 de 2010. 2010.
46. República de Colombia. Ley 1098 de 2006. Por la cual se expide el Código de la Infancia y la Adolescencia. 2006.
47. S FN, A JFC. Ética de la equidad y justicia en el acceso al diagnóstico, tratamiento y rERabilitación de los pacientes con enfermedades raras. Revista Médica Clínica Las Condes. 2015;26(4):527-32.
48. McCabe C, Edlin R, Round J. Economic considerations in the provision of treatments for rare diseases. Adv Exp Med Biol. 2010;686:211-22.
49. Hughes-Wilson W, Palma A, Schuurman A, Simoens S. Paying for the Orphan Drug System: break or bend? Is it time for a new evaluation system for payers in Europe to take account of new rare disease treatments? Orphanet J Rare Dis. 2012;7:74.
50. Buchanan J, Wordsworth S, Schuh A. Issues surrounding the health economic evaluation of genomic technologies. Pharmacogenomics. 2013;14(15):1833-47.
51. Potter BK, Khangura SD, Tingley K, Chakraborty P, Little J. Translating rare-disease therapies into improved care for patients and families: what are the right outcomes, designs, and engagement approaches in health-systems research? Genet Med. 2016;18(2):117-23.
52. Pagidas K, Ying Y, Keefe D. Predictive value of preimplantation genetic diagnosis for aneuploidy screening in repeated IVF-ET cycles among women with recurrent implantation failure. J Assist Reprod Genet. 2008;25(2- 3):103-6.
53. Kontoghiorghe CN, Andreou N, Constantinou K, Kontoghiorghes GJ. World health dilemmas: Orphan and rare diseases, orphan drugs and orphan patients. World J Methodol. 2014;4(3):163-88.
54. Galton DJ, Galton CJ. Francis Galton: and eugenics today. J Med Ethics. 1998;24(2):99-105.
55. Institute of Medicine (US) Committee on Accelerating Rare Diseases Research and Orphan Product Development. Profile of Rare Diseases Washington (DC): National Academies Press (US); 2010 [Available from: https://www.ncbi.nlm.nih.gov/books/NBK56184/.
56. Correa C, Mallarino C, Pena R, Rincon LC, Gracia G, Zarante I. Congenital malformations of pediatric surgical interest: prevalence, risk factors, and prenatal diagnosis between 2005 and 2012 in the capital city of a developing country. Bogota, Colombia. J Pediatr Surg. 2014;49(7):1099-103.
57. Bernal J, Zarante I. [Malformations and congenital anomalies: impact and future]. Biomedica. 2009;29(1):7-8.
58. Battista RN, Blancquaert I, Laberge AM, van Schendel N, Leduc N. Genetics in health care: an overview of cu-rrent and emerging models. Public Health Genomics. 2012;15(1):34-45.
59. Emery J, Watson E, Rose P, Andermann A. A systematic review of the literature exploring the role of primary care in genetic services. Fam Pract. 1999;16(4):426-45.
60. Wilson BJ, Islam R, Francis JJ, Grimshaw JM, Permaul JA, Allanson JE, et al. Supporting genetics in primary care: investigating how theory can inform professional education. Eur J Hum Genet. 2016;24(11):1541-6.
61. Epstein CJ. Medical genetics in the genomic medicine of the 21st century. Am J Hum Genet. 2006;79(3):434-8.
62. Qureshi N, Modell B, Modell M. Timeline: Raising the profile of genetics in primary care. Nat Rev Genet. 2004;5(10):783-90.
63. Bernal J, Suárez-Obando F. La era genómica y proteómica de la medicina. Univ Méd 2007;48(2).
64. StrannEReim H, Wedell A. Exome and genome sequencing: a revolution for the discovery and diagnosis of monogenic disorders. J Intern Med. 2016;279(1):3-15.
65. Ussher JR, Elmariah S, Gerszten RE, Dyck JR. The Emerging Role of Metabolomics in the Diagnosis and Prognosis of Cardiovascular Disease. J Am Coll Cardiol. 2016;68(25):2850-70.
66. Lam MP, Ping P, Murphy E. Proteomics Research in Cardiovascular Medicine and Biomarker Discovery. J Am Coll Cardiol. 2016;68(25):2819-30.
67. Coughlin SS. Toward a road map for global -omics: a primer on -omic technologies. Am J Epidemiol. 2014;180(12):1188-95.
68. Herr TM, Bielinski SJ, Bottinger E, Brautbar A, Brilliant M, Chute CG, et al. A conceptual model for translating omic data into clinical action. J Pathol Inform. 2015;6:46.
69. Devuyst O, Knoers NV, Remuzzi G, Schaefer F, Board of the Working Group for Inherited Kidney Diseases of the European Renal A, European D, et al. Rare inherited kidney diseases: challenges, opportunities, and pers-pectives. Lancet. 2014;383(9931):1844-59.
70. Knox SS. From ‘omics’ to complex disease: a systems biology approach to gene-environment interactions in cancer. Cancer Cell Int. 2010;10:11.
71. Gligorijevic V, Malod-Dognin N, Przulj N. Integrative methods for analyzing big data in precision medicine. Proteomics. 2016;16(5):741-58.
72. Underwood JC. More than meets the eye: the changing face of histopathology. Histopathology. 2017;70(1):4-9.
73. Marincola FM. Translational Medicine: A two-way road. J Transl Med. 2003;1(1):1.
74. Swinney DC, Xia S. The discovery of medicines for rare diseases. Future Med Chem. 2014;6(9):987-1002.
75. Groft SC. Rare diseases research: expanding collaborative translational research opportunities. Chest. 2013;144(1):16-23.
76. Everett JR. From Metabonomics to Pharmacometabonomics: The Role of Metabolic Profiling in Personalized Medicine. Front Pharmacol. 2016;7:297.
77. Sankar PL, Parker LS. The Precision Medicine Initiative’s All of Us Research Program: an agenda for research on its ethical, legal, and social issues. Genet Med. 2016.
78. Adams SA, Petersen C. Precision medicine: opportunities, possibilities, and challenges for patients and providers. J Am Med Inform Assoc. 2016;23(4):787-90.
79. Singh G, Schulthess D, Hughes N, Vannieuwenhuyse B, Kalra D. Real world big data for clinical research and drug development. Drug Discov Today. 2017.
80. Luscombe NM, Greenbaum D, Gerstein M. What is bioinformatics? A proposed definition and overview of the field. Methods Inf Med. 2001;40(4):346-58.
81. Suarez-Obando F, Ordoñez A. Aspectos éticos de la informática médica: principios de uso y usuario apropiado de sistemas computacionales en la atención clínica. Acta Bioethica. 2012;18(2):199-208.
82. Lorenzi NM. The cornerstones of medical informatics. J Am Med Inform Assoc. 2000;7(2):204-5.
83. Suarez-Obando F, Gómez-Restrepo C, Camacho J, de la Hoz A, Ruiz A, Maldonado P, et al. Portal de Guías de Práctica Clínica: estrategia digital (e-learning) para la difusión de guías de práctica desarrolladas en Co-lombia Desarrollo de una estrategia educativa y de difusión de Guías desarrolladas en Colombia. Univ Méd. 2016;57(1).
84. Belle A, Thiagarajan R, SoroushmERr SM, Navidi F, Beard DA, Najarian K. Big Data Analytics in Healthcare. Biomed Res Int. 2015;2015:370194.
85. Tenenbaum JD. Translational Bioinformatics: Past, Present, and Future. Genomics Proteomics Bioinformatics. 2016;14(1):31-41.
86. Butte AJ, Ohno-Machado L. Making it personal: translational bioinformatics. J Am Med Inform Assoc. 2013;20(4):595-6.
87. Day S. Evidence-based medicine and rare diseases. Adv Exp Med Biol. 2010;686:41-53.
88. Gupta S, Faughnan ME, Tomlinson GA, Bayoumi AM. A framework for applying unfamiliar trial designs in studies of rare diseases. J Clin Epidemiol. 2011;64(10):1085-94.
89. Abrahamyan L, Feldman BM, Tomlinson G, Faughnan ME, Johnson SR, Diamond IR, et al. Alternative designs for clinical trials in rare diseases. Am J Med Genet C Semin Med Genet. 2016;172(4):313-31.
90. Kalita-de Croft P, Al-EjER F, McCart Reed AE, Saunus JM, Lakhani SR. ‘Omics Approaches in Breast Cancer Research and Clinical Practice. Adv Anat Pathol. 2016;23(6):356-67.
91. Fragoulakis V, Mitropoulou C, van Schaik RH, Maniadakis N, Patrinos GP. An Alternative Methodological Approach for Cost-Effectiveness Analysis and Decision Making in Genomic Medicine. OMICS. 2016;20(5):274- 82.
92. Knoppers BM, Leroux T, Doucet H, Godard B, Laberge C, Stanton-Jean M, et al. Framing genomics, public health research and policy: points to consider. Public Health Genomics. 2010;13(4):224-34.
93. Frieden TR. SHATTUCK LECTURE: The Future of Public Health. N Engl J Med. 2015;373(18):1748-54.
94. Llamas B, Willerslev E, Orlando L. Human evolution: a tale from ancient genomes. Philos Trans R Soc Lond B Biol Sci. 2017;372(1713).
95. Cousineau J, Girard N, Monardes C, Leroux T, Jean MS. Genomics and public health research: can the state allow access to genomic databases? Iran J Public Health. 2012;41(5):13-30.
96. Wilkinson JR, Ells LJ, Pencheon D, Flowers J, Burton H. Public health genomics: the interface with public health intelligence and the role of public health observatories. Public Health Genomics. 2011;14(1):35-42.
97. Gjesing AP, Pedersen O. ‘Omics’-driven discoveries in prevention and treatment of type 2 diabetes. Eur J Clin Invest. 2012;42(6):579-88.
98. Taruscio D, Vittozzi L, Choquet R, Heimdal K, Iskrov G, Kodra Y, et al. National registries of rare diseases in Europe: an overview of the current situation and experiences. Public Health Genomics. 2015;18(1):20-5.
99. Vittozzi L, Gainotti S, Mollo E, Donati C, Taruscio D. A model for the European platform for rare disease registries. Public Health Genomics. 2013;16(6):299-304.
100. Lautenschlager R, Kohlmayer F, Prasser F, Kuhn KA. A generic solution for web-based management of pseudonymized data. BMC Med Inform Decis Mak. 2015;15:100.
101. Viviani L, Zolin A, MERta A, Olesen HV. The European Cystic Fibrosis Society Patient Registry: valuable lessons learned on how to sustain a disease registry. Orphanet J Rare Dis. 2014;9:81.
102. Kinkorova J. Biobanks in the era of personalized medicine: objectives, challenges, and innovation: Overview. EPMA J. 2015;7:4.
103. Singh V, Braddick D, Dhar PK. Exploring the potential of genome editing CRISPR-Cas9 technology. Gene. 2017;599:1-18.
104. Zomer HD, Vidane AS, Goncalves NN, Ambrosio CE. Mesenchymal and induced pluripotent stem cells: general insights and clinical perspectives. Stem Cells Cloning. 2015;8:125-34.
Recibido: 22 de enero de 2018
Aceptado: 20 de febrero de 2018
Correspondencia:
Fernando Suárez Obando
fernando.suarez@javeriana.edu.co
