Sus posibilidades en el diagnóstico, como criterio pronóstico y para la detección de la enfermedad residual
Jorge J. Yunis, M. J) *
Introducción
Se ha demostrado claramente que en pacientes con enfermedades neoplásicas existen frecuentemente reordenamientos genómicos específicos. Uno de los mecanismos de transformación mejor entendido es el que tiene lugar en un gran número de leucemias y linfomas del tipo no-Hodgking.
En ellos se ha observado la existencia de un defecto específico estructural clonal a nivel cromosómico. Frecuentemente, el defecto consiste en una translocación recíproca, con dos puntos de ruptura muy precisos. Uno de estos puntos de ruptura se sitúa en el lugar de un proto-oncogén que se desregula por causa del reordenamiento cromosómico.
Esta falta de regulación, después del reordenamiento, es de efecto dominante, en el que un proto-oncogén se transforma en oncogén.
Con el reordenamiento cromosómico puede resultar que el segmento de un proto-oncogén se fusiona con el segmento de otro gen en el segundo cromosoma, creando un defecto único o específico de cáncer en el cual el nuevo gen híbrido produce una proteína de fusión (por ejemplo la fusión de los genes BCRI ABL in la t(9;22)) de la leucemia mieloide crónica.
Alternativamente el proto-oncogén de un cromosoma se desregula por su proximidad a una secuencia reguladora de otro gen en el segundo cromosoma. En este caso el proto-oncogén convertido en oncogén mantiene la estructura proteica normal pero se produce anormalmente (por ejemplo MYC an la t(8;14)) en ellinfoma de Burkitt.
Anivel clínico, el análisis cromosomal es un instrumento de diagnóstico eficaz. Por ejemplo, cuando se utilizó el análisis cromosómico de alta resolución en un estudio de más de 800 pacientes con cáncer, llevado a cabo en nuestro laboratorio, se pudo determinar que las células malignas de la mayor parte de los tumores analizados (94%)tenían un defecto cromosomal específico. Una translocación o la pérdida de una banda cromosómica o segmento (delección) fueron los defectos más comunes.
Con menos frecuencia se encontró una trisomía o una inversión. Tales defectos son tan importantes en las enfermedades hematológicas, que han hecho posible que se puedan subdividir las leucemias y los síndromes mielodisplásicos en categorías importantes desde el punto de vista pronóstico. También los linfomas del tipo no-Hodgkin pueden ser divididos en varios subgrupos de importancia biológica y clínica. (Lea también: Litotricia Extracorpórea, Generación de Ondas de Choque)
Leucemia Mieloide Crónica
En 1960 se observó la existencia de un cromosoma muy pequeño en las leucemias mieloides crónicas (LMC). Este cromosoma empezó a designarse con el nombre del cromosoma Filadelfia. Este fue el primer defecto cromosómico encontrado en células malignas humanas, que más tarde se identificó como el resultado de una translocación t(9;22) (q34.1;qll.21).
Una translocación t(9;22) se ha observado en aproximadamente-el 90-95%en adultos que se diagnosticaron clínicamente con LMC.Este defecto se encuentra a lo largo de la evolución de la enfermedad.
La presencia de t(9;22) en LMC es un indicador útil, porque estos pacientes tienen una media de sobrevivencia de 42 meses, mientras que el resto (5 al 10%) de los pacientes con LMC que no tienen tal defecto, sobreviven como media solamente unos 15 meses.
Se ha demostrado que el oncogén Abelson (ABL), que pertenece a la familia de cinasas de tirosina y está normalmente localizado en la banda 9q34, se reorganiza con el gen BCR del cromosoma 22, produciendo un transcrito anormal que origina una proteína de naturaleza híbrida BCR-ABL.
Después de ser tratado un paciente con LMC, se puede detectar si exíste enfermedad residual usando la técnica “RCP” o de “reacción en cadena de la polimer< L<;a”la, cual puede detectar si existen células leucémicas residuales con producción de RNA de naturaleza híbrida nCR-ABL.
Recientemente hemos adaptado esta técníca para demostrar cuantitativamente la evolución de la enfermedad, después del tratamiento de transplante de médula ósea, para saber prontamente si el paciente está curado o puede tener una recurrencia. Esta técnica detecta cuantítatívamente ha”ta una célula leucémica en un millón de células normales.
Leucemia Mieloide Aguda
El análisis de los cromosomas de la médula ósea también puede servir como indicador independiente del pronóstico de la mayor parte de los pacientes con leucemia mieloide aguda (LMA).Por ejemplo, en nuestro laboratorio hemos encontrado ocho categorías cromosómicas frecuentes mediante el análisis en alta resolución cromosómica en médula ósea de 194 pacientes adultos consecutivos con leucemia mieloide aguda de tipo primario
Se hallaron tres grupos de pacientes con pronóstico relativamente favorable que tenían ya sea una inversión en el cromosoma 16, una transloc’ación t(8;21) o cromosomas normales. Los pacientes en estos grupos tenían una media de sobrevivencia de 22 meses o más y aproximadamente el 62”(,de los pacientes todavía están vivos.
Un cuarto grupo de pacientes tenía anormalidades cromosómícas complejas y un pronóstico bastante pobre. Un quinto grupo de pacientes con una translocación t( 15;17) exclusivamente asociados con el subtipo de leucemia promielocítica aguda tenía una media de sobrevivencia de 20 meses.
En este quinto grupo, el gen RARa que codifica al receptor alfa del ácido retinoico (un gen de regulación de la transcripción, importante en la diferenciación celular mieloide) es truncado por la translocación t(l5;17).
La translocación t(l5;17) fusíona el dominio “Zinc finger” o “dedo de zinc” en el extremo c-terminal del gen RARa, localizado en el cromosoma 17, con la región que codifica al extremo amino terminal del gen PML, presente en el cromosoma 15. El resultado es una proteína de fusión PMURARA. Otras translocaciones asociadas con LMA también se han encontrado recientemente involucrando genes reguladores de transcripción, formando una proteína híbrida como es el caso de la translocación t(6;9) con la fusión DEKlCAN.
La proteína de los genes reguladores se une a secuencias específicas de ADN a través de la región HLH.Esta unión puede formar homodímeros o heterodímeros con otras proteínas. Heterodímeros muestran diferentes especificidades cuando se comparan con los homodímeros. Esto hace posible la unión de los heterodímeros a un gran número de secuencias blanco y proveen un nivel de regulación más fina.
En los casos con LMA primarios una translocación específica o una inversión parece ser el defecto dominante y la enfermedad aparece generalmente de forma repentina sin haber manifestado un estadio pre-leucémico detectable clínicamente. Estos defectos tienen una etiología desconocida, se presentan en la mayoría de los casos en individuos entre 40 a 60 años y generalmente no van acompañados de otros defectos cromosómicos en el momento del díagnóstico.
Al contrario de la mayoría de los pacientes que llevan una translocación recíproca, los pacientes con trisomía 8 o una monosomía 5 o 7 tienen frecuentemente una historia preleucémica o dispoiesis sanguínea. Van acompañados en el momento del diagnóstico o durante la evolución de la enfermedad con otros cambios cromosómicos o de una mutación de punto en uno de los oncogenes RAS.
En los casos LMA con monosomía 7 o deJección 7q. encontrados de forma única o asociados con otros defectos, aparentemente las células madres (stem cell) están afectadas, y esto puede explicar la resistencia a los tratamientos y los pronósticos tan pobres que se observan en este grupo de pacientes. Además, las delecciones 5q y 7q, al igual que otros defectos cromosómicos se asocian con edades avanzadas (media de 69 años) y con la exposición ocupacional o ambiental a la radiación o carcinógenos químicos.
Síndromes Mielodisplasicos
Los síndromes mielodisplásicos primarios (SMD) se observan frecuentemente en pacientes con más de 60 años de edad. Aproximadamente del 20 al 30% de los mismos desarrollan LMAy un número igual muere, por falta de médula, dentro de los dos años a partir del diagnóstico. El resto tiene una media de sobrevivencia relativamente larga aun utilizando tratamientos sintomáticos.
Usando análisis cromosómico en médula de 100 pacientes adultos consecutivos con síndrome mielodisplásico primario, hemos encontrado cinco categorías cromosómicas frecuentes con diferencias de sobrevivencia marcada. En la primera categoría, el 27~) de los pacientes tenían cromosomas normales, un curso clínico estable que requiere solamente tratamiento sintomático y una larga tasa de sobrevivencia.
Una segunda categoría estaba compuesta por el 12%de los pacientes que tenían una monosomía 7 única o una delección 7q con una media de sobrevivencia de 7 meses. Estos pacientes tienen en común una delección del segmento cromosómico 7q32q36.
Es importante destacar que el 72X, de los pacientes con monosomía 7/del 7q bien de forma única o con defectos adicionales evolucionaron a MLAo a SMD de naturaleza clínica más agresiva. Esto contrasta con el hecho de que solamente el 26%de todos los otros pacientes tuvieron tal evolución.
Defectos cromosómicos complejos se encontraron en el 19%de todos los pacientes y estaban asociados con un pronóstico bastante desfavorable (media de sobrevivencia de 3 meses). En esta categoría todos los pacientes murieron después de haber evolucionado a MLA. El 88% de estos pacientes tenían una delección 5q o una monosomía 5q o una monosomía 5.
El 58% tenía una delección 7q o una monosomía 7 y el 32% una monosomía o parcial delección del brazo largo del cromosoma 20. La trisomía 8 como único defecto cromosómico se encontró en el 10% de los pacientes con una media de sobrevivencia de 18 meses. También el 8% de los pacientes tenía una pequeña delección única 5q, teniendo en común una delección del segmento cromosómico 5q31q35 y una prolongada tasa de sobrevivencia.
En forma parecida a la leucemia mieloide aguda, aproximadamente un 40 por ciento de SMD tiene una mutación de punto de un proto-oncogén RAS que parece predisponer a los pacientes a un fenotipo monocítico agresivo.
Una quinta parte de los pacientes con SMD primarios tenían un historial de haber sido expuestos a carcinógenos químicos o a radiación. Los defectos cromosómicos recurrentes encontrados en la mayoría de los pacientes con SMDprimarios (pérdida única completa o parcial del cromosoma 5 y 7, trisomía 8 o defectos cromosómicos complejos), han sido también encontrados en pacientes con SMDy LMAque habían sido tratados con radiación o quimioterapia anteriormente al desarrollo del proceso hematológico.
Leucemia Linfoide Aguda
Leucemias linfoides agudas (LLA) han sido diagnosticadas fundamentalmente por criterios morfológicos y marcadores inmunológicos. Estos estudios han sugerido que los pacientes diagnosticados como LLA-L1o como fenotipo T y B negativo (precursores de células B) tienen un pronóstico mejor que los que han sido diagnosticados morfológicamente como L2 o L3 o con fenotipo celular T o B.
Se debe indicar, sin embargo, que los pacientes con LLA-Ll o fenotipo T y B negativo representan el 85% de todos los pacientes LLA y que estos grupos son heterogéneos desde el punto de vista cromosomal.
Once categorías cromosomales frecuentes e importantes desde el punto de vista pronóstico se han identificado. Incluyen pacientes con cromosomas normales, hiperploidía con 51 a 60 cromosomas, hiperploidía con 47 a 50 cromosomas y un tipo de aploidía (26 a 39 cromosomas), delección 6q, una delección o translocación con un punto de ruptura en la banda 12p12 y 5 translocaciones recíprocas específicas.
Una de las 11 categorías está particularmente asociada con procesos clínicos de seguimiento de tipo largo. Esta categoría incluye pacientes con hiperploidía (11 a 20%de los casos LLA;).Los pacientes de esta categoría han sido diagnosticados de forma variable comn LLA-L1 o L2, tienen un fenotipo precursor de células B, y una media de sobrevivencia de más de 36 meses en niños y más de 21 meses en adultos.
Las anormalidades numéricas encontradas de ordinario llevan consigo extra cromosomas 4, 6, 10, 14, 17, 18, 21, y X con un extra cromosoma 6 y 21 en casi todos los casos. Generalmente de dos a seis de estos cromosomas recurrentes se ven en la mayoría de los pacientes.
Este grupo de buen pronóstico clínico contrasta con los pacientes que tienen una de 5 translocaciones recíprocas recurrentes, quienes, de ordinario, responden poco a los tratamientos y tienen un pobre pronóstico.
Estos defectos incluyen las translocaciones t(l;19)( q23;p13); t(8;14)( q24;q32); t(9;22)(q34q11); t(4;11)(q21q23); t(V;12)(V;p12); Y t(11;14)(p13;q11). Excepto en pacientes con una translocación t(8;14), que son diagnosticados como LLA-L3,todas las demás translocaciones han sido descritas como LLA-L1o L2.
Translocaciones específicas se encuentran en aproximadamente un tercio de todos los casos LLA y su identificación es de vital importancia. Dado que la respuesta a los tratamientos quimioterápicos estándar es muy pobre, tales pacientes necesitan tratamientos agresivos como es el transplante de médula ósea que se emplea en este grupo de pacientes.
Todos estos estudios indican que el análisis cromosomal debe ser de uso rutinario y un factor importante a tener en cuenta si se quiere hacer un tratamiento adecuado ya sea de los casos LLA,LMA o SMD.
Algunas de las translocaciones que se encuentran en los casos LLAproceden de mecanismos moleculares similares a los indicadores en el linfoma de Burkitt y en las leucemias mieloides agudas que envuelvan a genes reguladores de tanscripción (Tabla 1).
Por ejemplo, estudios recientes han indicado que el oncogén c-MYC y los genes IgH están reorganizados y se expresan anormalmente en los casos LLAt(8;14) positivos. En pacientes LLAt(9;22) positivos se ha descrito la existencia de una variante molecular del reordenamiento del oncogén ABL y el gen BCR para producir una molécula híbrida de RNA y proteína un poco diferente de la que se encuentra in LMC.
Además la translocación t(1:19) (q23;p13.3) encontrada en leucemias linfocíticas agudas pre B, en niños, produce una nueva proteína quimérica, generada por la fusióndel gen E2A en el cromosoma 19 (este gen codifica las proteínas E12 y E47, las cuales se unen normalmente al aumentador o “enhancer” de los genes de las inmunoglobulinas), con la región homeótica (homeobox) del gen PBX, mapeado en el cromosoma 1.
El gen PBX, normalmente no se expresa en células pre-B, mientras que la proteína quimérica originada por la translocación se expresa constitutivamente en las células leucémicas (Tabla 1).
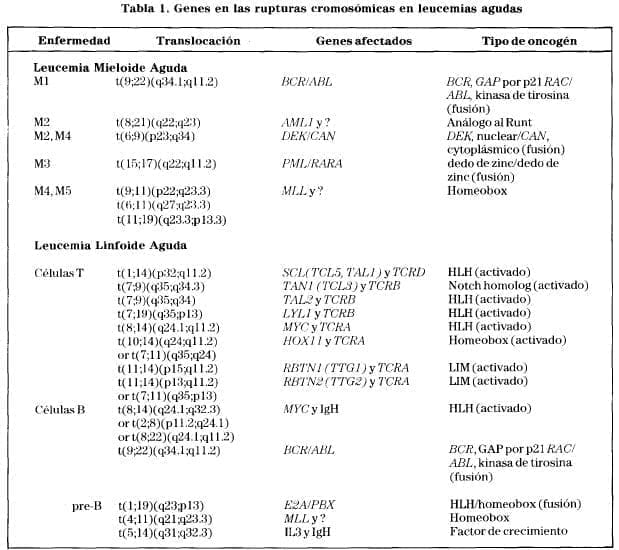
Otro ejemplo es el del gen LYL-1 en el cromosoma 19, el cual es translocado (en una configuración “cabeza a cabeza”) a la región del gen del receptor beta de células T, localizado en el cromosoma 7, resultando en la síntesis de un RNA mensajero truncado en LLA-Tcon translocación t(7;19)(q35;p13). Esta proteína, que parece ser reguladora de transcripción, contiene una región que se une a DNA en su dominio HLH.
De manera similar, el gen TTG-1, codifica a una proteína con una región “dedo de zinc” o “zinc fmger”, que se une a DNA y se ha encontrado re arreglada con la región del gen delta-TCR-o en una translocación t(11;14) (p15;q11.2).
Otro miembro de la familia HLH afectado en otro sub grupo de LLA-T, es el gen SCL, localizado en el cromosoma 1,el cual se rearregla con el gen delta-TCR-o en el cromosoma 14 en la translocación t(l;14)(p33;q32). Alternativamente SCL se puede fusionar con otro gen llamado SIL vía una delección intersticial lp33. En cualquier caso se origina un tránsito fusionado con una ex- presión alterada, pero la proteína codificada por la región SCL no se afecta.
Linfomas del tipo no-Hodgkin
Linfomas Burkitt y Trastornos Relacionados
El linfoma de Burkitt representa el primer tipo de linfoma del tipo no-Hodgkin (NHL) que ha sido caracterizado citogenéticamente. En esta severa enfermedad de células linfoides B se ha encontrado frecuentemente una translocación cromosómica recíproca t(8;14) con puntos de ruptura en las bandas 8q24.1 y 14q32.3 (aproximadamente el 75% de los pacientes).
El oncogén c-MYC se traslada de su localización normal en la banda 8q24.1 y se desregula cuando se reordena, a partir del 5′ terminal, con la región J o S de uno de los genes constantes de la cadena pesada de la inmunoglobulina (IgH) en la banda 14q32.3. Con menor frecuencia (el 25% de los pacientes), el oncogén MYC se reordena con los genes kappa o lambda que codifican para la cadena ligera de las inmunoglobulinas de un cromosoma 2 o 22 t(2;8)(p11.2;q24.1) Y t(8;22)( q24.1;q11.2), respectivamente.
El gen c-MYC produce una proteína que contiene una región reguladora de transcripción que se une a DNA en su dominio de hélice-asa-hélice [helixloop- helix (HLH)]. Normalmente c-MYC está involucrado en la proliferación celular y activa la transición de la fase Go a la fase G¡ del ciclo celular. Se desregula en translocaciones recíprocas en células B o T en linfomas y leucemias y por amplificación y expresión aumentada en estadios avanzados de varias enfermedades malignas.
Junto a la región HLH, la proteína MYC tiene un segmento de aminoácidos básicos y la región zipper de leucina también dimeriza con MAX y otras proteínas. El mecanismo detallado de regulación no se conoce. Sin embargo, parece ser importante la ruptura del equilibrio normal de dimerización de MYC en el linfoma Burkitt.
La translocación t(8; 14) o una de las variantes mencionadas se encuentra tanto en los linfomas Burkitt positivos y negativos para el virus Epstein-Barr (VEB) como en LLA-L3.También hemos encontrado esta translocación en los linfomas del tipo no Burkitt de células pequeñas difusas y en un linfoma ínmunoblástico de células B.
Estos resultados han sido confinnados por otros investigadores. Ellinfoma de Burkitt es más frecuente en Africa Central y está asociado con áreas donde la malaria y la infección VEB es endémica. Aunque el linfoma de Burkitt se encuentra también en Europa y en USA,no se asocia con malaria o VEB, y es posible que estos factores, cuando están presentes, puedan seIVir para disminuir la respuesta del sistema inmune y facilitar la transformación y proliferación clonal de células B.
Linfoma Folicular
Varias anormalidades cromosómicas específicas se han encontrado en NHL y en LLC. La más común en NHL es la translocación t(l4;18)(q32.3;q21.3) que se encuentra en el 85%de todos los linfomas foliculares o en el 40% de todos los linfomas del tipo no-Hodgkin. En la translocación t(l4;18), el oncogén BCL-2 del cromosoma 18 se reorganiza y coloca a la izquierda de la región J del locus IgH del cromosoma 14.
El gen BCL-2 se puede desregular por la acción de un elemento amplificador que se encuentra entre la región J y la región control de los genes IgH. Curiosamente, el oncogén BCL-2 codifica una proteína de la membrana interna de las mitocondrias y su desregulación resulta en una vida prolongada de las células B.
Además de la translocación t(l4;18), 15 anormalidades cromosómicas específicas se encontraron en un estudio longitudinal de 71 pacientes consecutivos con linfoma folicular. En 10 de ellos, estas anormalidades cromosómicas parecen influir en la histopatología, el curso clínico y la respuesta al tratamiento.
La translocación t(l4;l8) parece ser el principal determinante de la estructura folicular y en diez pacientes se presentó corno defecto único asociado con histología folicular de células partidas pequeñas (FSC). La mayor parte de estos pacientes no requirieron tratamiento los dos primeros años de la enfermedad.
Esto sugiere que este tipo de tumor tiene un curso indolente. Pacientes FSC con la translocación t(l4;18) y la delección del 13q32 generalmente desarrollan una leucemia sanguínea y la enfermedad tiene un curso muy acelerado.
La delección 6q y una trisomía parcial o completa del cromosoma 7 y/o del cromosoma 12 se asoció con tipos histológicos clínicos más agresivos de células grandes y pequeñas mezcladas (FMC) o de células largas únicamente (FLC). Estos tipos histológicos frecuentemente han sido antes FSC. Una trisomía parcial o completa de cromosoma 3, del cromosoma 18 y del cromosoma 21 se correlaciona casi exclusivamente con FLC.
En algunos pacientes también se ha detectado a nivel cromosómico y molecular que puede existir una t(l4;18) con re ordenamiento BCL-2/lgH combinado con una t(8;14) con rearreglo c-MYC/lgH.
También hemos encontrado que en la evolución del linfoma a un nivel más avanzado, puede aparecer un reordenarniento o una amplificación del proto-oncogén hc-REL, consistiendo en una delección o de una región de tinción homogénea (HSR) en el segmento cromosómico 2pll.2p13, donde se ha mapeado hc- REL. El gen hc-REL pertenece a una familia de reguladores de transcripción en la cual se encuentra NF-KB,que regula la expresión de una variedad de genes en diferentes tejidos.
Leucemia Linfoide Crónica
Los linfomas bien diferenciados de células pequeñas o linfomas linfoides pequeños (LLP) y tipos leucémicos asociados [leucemias linfoides crónicas (ILC)] representan un grupo heterogéneo de enfermedades.
En LLCde células B, por ejemplo, algunos pacientes llevan una trisomía 12 corno defecto cromosómico único y larga sobrevivencia, mientras que un subgrupo variante tiene una translocación t(l1;14) (q13;q32) con re arreglo del oncogén BCL-1 y IgH, el cual generalmente tiene corta sobrevivencia. También hemos observado que los pacientes con una delección del (1l)(q14.2q24.2) desarrollan un curso clínico más progresivo, son refractarios a los tratamientos y tienen un tiempo de sobrevivencia menor.
Lo mismo sucede con la presencia de defectos cromosómicos múltiples superimpuestos sobre + 12 o t(l1;14), lo cual tiene una influencia importante en disminuir el tiempo de sobrevivencia de los pacientes del tipo de células B.
En LLP y LLC de células T se puede encontrar la translocación t(2;14)(p13;q11.2), la translocación t(8;14) (q24.l;q11.2) o la translocación t(l4;14)(q11.2;q32.3). La translocación t(l4;14)( q11.2;q32.3) se ha encontrado no solamente en casos con LLP o LLC de células T sino también en pacientes con enfermedades relacionadas de tipo fúngico (micosis) y en el síndrome de Sézary. En el caso de una translocación t(8;14)(q24.1;q11.2) el oncogén c-MYC se reorganiza con los genes receptores alfa de células T.
Detección de la Enfermedad Residual a Nivel Molecular
En un número grande de leucemias y linfomas existe una fusión específica de dos genes a nivel de la transcripción.
El uso de la técnica RT-PCR transcriptasa de reverso-reacción en cadena de la polirnerasa hace posible la detección específica de estos transcritos de fusión (Tabla 2).
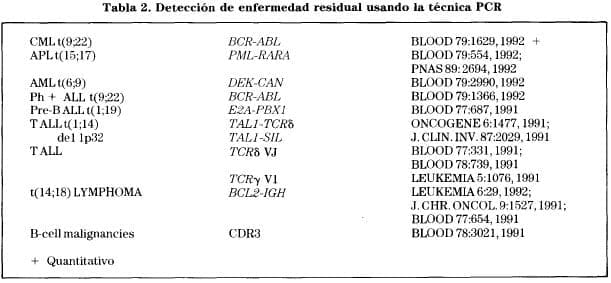
Estas técnicas también han aumentado la detección de la enfermedad residual y es posible demostrar la presencia de una célula maligna mezclada con un millón de células normales. Tomando ejemplos de un paciente en diferentes tiempos después de obtenerse una remisión clínica completa, es posible demostrar si se aumenta el número de moléculas anormales indicando la presencia de un relapso temprano.
Conclusión Final
El análisis cromosómico desempeña un papel crítico e importante en el diagnóstico, pronóstico y tratamiento de las neoplasias de tipo sanguíneo. La mayor parte de los pacientes con LMA y LLA pueden ser incluidos en una de tres categorías fundamentales de pronóstico. Es necesario determinar el valor de los tratamientos usuales tomando en consideración estudios cromosómicos.
Creemos ademá.” que los pacientes que están dentro de categorías cromosámicas específicas deben ser tratados con tipos de terapia también específicos en un intento de mejorar la tasa de sobrevivencia.
Paralelo a lo que ocurre en las leucemias, en los tumores sólidos malignos y linfomas de tipo no- Hodgkin la detección de defectos cromosómicos múltiples recurrentes es crucial para entender el proceso carcinogénico. Por otro lado, ya se han determinado los procesos moleculares cruciales en varias enfermedades hematológicas y esto es de considerable importancia para el entendimiento de la patogenia del cáncer y eventualmente en el tratamiento.
Como se ejemplificó con la cuantificación de la expresión del gen híbrido BCR-ABL en LMC, ya es posible estudiar la evolución de la enfermedad post-tratamiento, para conocer si el paciente está totalmente curado o tendrá una recaída. Estudios para encontrar la utilidad en el análisis de otros genes híbridos está en progreso en varios laboratorios.
Recientemente se ha encontrado que un buen número de defectos de oncogenes involucran a aquéllos que participan en la regulación de la transcripción de otros genes celulares. El análisis detallado de estos genes hará posible que se pueda conocer más profundamente la regulación de los procesos celulares involucrados no sólo en el cáncer sino también en la embriogénesis y la diferenciación celular normal.
Referencias
1. YUNIS,J. J. (1983): The chromosomal basis of human neoplasia. Science 221: 227-236.
2. YUNIS, J. J. and TANZER, J. (1992): Molecular mechanisms ofhematologic malignancies. Critical Reviews in Oncogenesis. (In press).
3. THOMPSON, J. D.; BRODSKY, 1. and YUNIS, J. J. (1992): Molecular quantification ofresidual disease in chronic myelogenous leukemia after bone marrow transplantation. Blood 79(6): 1629-1635.
4. YUNIS J. J.: Genes and chromosomes in the pathogenesis and prognosis of human cancer. In Advances in Pathology. Vol. 2, pp. 147-188, 1989. C. Fenoglio-Preiser et al ed. Year Book Publishers Inc.
, Profesor y Vice-Jefe del Departamento de Enfermedades Neoplasias Universidad de Hahnemann, Filadelfia, Pensilvania; USA
